
El desarrollo de la bioinformática es el resultado de los avances tanto en biología molecular como en ciencias computacionales a lo largo de los últimos 30-40 ańos.Tiene su origen en los ańos 1950’s cuando se logró comprender la estructura tridimensional del ADN, la molécula responsable de transmitir la herencia genética.

A finales de los ańos 50 el mundo académico (en Estados Unidos, se entiende) empezó a tener acceso no restringido a los ordenadores, que hasta ese momento sólo habían tenido un uso militar; Estos ordenadores estaban basados en válvulas de vacío, y se programaban a bajo nivel (no se podían reutilizar los programas), pero ayudaron a comenzar el desarrollo de técnicas computacionales y de desarrollo de software en el mundo académico.
Mayo de 1952, Rosalind Franklin obtiene la famosa fotografía 51, una imagen del ADN obtenida mediante difracción de rayos X.
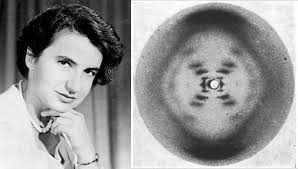
La fotografía 51 es una de las fotografías mas famosas en la historia de la biología, es una foto del secreto de la vida, como la llamaron en ese entonces los periódicos. Es, con más precisión, una fotografía de la molécula ADN B, y es la evidencia clave que demuestra que el ADN tiene forma helicoidal.
Abril de 1953, James D. Watson y Francis Crick reportan la estructura tridimensional del ADN (modelo de doble hélice).


James Watson y Francis Crick transformaron la biología con su descubrimiento del ADN en 1953, y dieron el primer paso para lo que serían después los avances del genoma humano y la clonación de organismos. Pero la historia de la doble hélice esconde mucho más que el trabajo arduo de dos científicos.
Ninguno de los dos científicos era biólogo. Watson, era un zoólogo estadounidense, mientras Crick era un físico inglés. Para 1951, ambos impetuosos, arrogantes y altamente competitivos, decidieron trabajar juntos en el Cavendish Laboratory (Cambridge, Inglaterra), para resolver uno de los problemas clave en la biología de aquella época: el ADN y su capacidad para codificar la información.
Watson y Crick hicieron su mejor esfuerzo para no dejarse ganar la carrera por el famoso químico estadounidense Linus Pauling. Pauling estaba a punto de abordar un avión a Inglaterra en mayo del 52 para lograr acceso a rayos X detallados del ADN, cuando el gobierno de Estados Unidos le retuvo el pasaporte argumentando sus actividades antiamericanas.
Las imágenes de rayos X habían sido creadas por Maurice Wilkins y Rosalind Franklin. Estos científicos ayudaron a descifrar el código, pero su aversión mutua bloqueó la colaboración. Franklin, una de las pocas mujeres en investigación, fue tan relegada que decidió retirarse. Wilkins le mostró a Watson una de las imágenes del ADN de Franklin sin su aprobación y ese fue el momento de la iluminación: Watson se dio cuenta de que los patrones formados en cruz en la fotografía tenían que estar formados como una hélice. Así, conjuntamente con Crick, construyó un modelo de metal de dos hélices unidas entre sí por pares de cuatro moléculas.
El reporte sobre el modelo en la publicación Nature, en 1953, dio a ambos, Watson y Crick, conjuntamente con Wilkins, el premio Nóbel de Medicina en 1962. Franklin, olvidada, murió de cáncer en 1958.
Probablemente el primer proyecto Bioinformática fue llevado a cabo por Margaret Dayhoff en 1965, quien desarrolló la primera BD de secuencias de proteínas.


Una de las pioneras de la Bioinformática. Ella comenzó con una preparación en química cuantitativa y matemáticas, y alrededor de los ańos 60 empezó a estar interesada en el mundo de las proteínas y la evolución molecular. Tuvo un buen punto de partida para sus intereses científicos, al ser en aquella época directora asociada de la recién creada National Biomedical Research Foundation, una fundación interesada en la promoción y aplicación de las técnicas computacionales para ayudar en la investigación médica. Margaret Dayhoff empezó a explorar las distintas técnicas matemáticas para analizar los ya crecientes datos de secuencias de aminoácidos.

Dayhoff fundó el Atlas of Protein Sequence and Structure (atlas de secuencia y estructura de proteínas), una publicación anual que intentaba catalogar todas las secuencias de aminoácidos conocidas. De forma muy rudimentaria, ésta fue la primera base de datos de información sobre biología molecular, y se convirtió en el recurso indispensable para las primeras investigaciones computacionales.
Con el paso del tiempo (y la creación de internet y la web) esta publicación evolucionó hasta convertirse en 1983 en una de las principales bases de datos online, PIR (the Protein Information Resource). Se convirtió en un importante punto de partida, y un referente para la creación de otras bases de datos basadas en información molecular.
Al inicio de los ańos 1970, el Laboratorio Nacional de Brookhaven (USA) estableció el Banco de Datos de Proteínas para almacenar estructuras de proteínas en 3D (12 al inicio, 90,611 al día de hoy).
El primer algoritmo para alineamiento de secuencias fue desarrollado por Needleman y Wunsch en 1970.
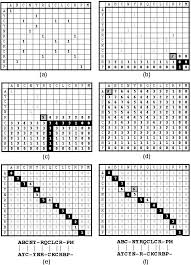
Este fue un paso fundamental en el desarrollo del campo de la bioinformática, que abrió el camino para las comparaciones de secuencias y búsquedas en BD de rutina realizadas por los biólogos modernos; Se suele utilizar en el ámbito de la bioinformática para alinear secuencias de proteínas o de ácidos nucleicos.
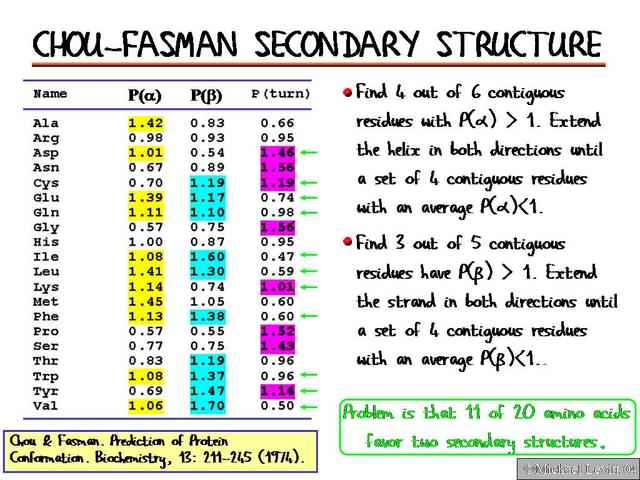
El primer algoritmo para predicción de estructuras de proteínas fue desarrollado por Chou y Fasman en 1974.
Los ańos 1980 vieron el establecimiento del GenBank y el desarrollo de rápidos algoritmos para búsquedas en BD como FASTA de William Pearson y BLAST de Stephen Altschul et al.
BLAST es un programa informático de alineamiento de secuencias ADN, ARN o de proteinas. El programa es capaz de comparar una secuencia problema (también denominada en la literatura secuencia query) contra una gran cantidad de secuencias que se encuentren en una base de datos.
FASTA es un programa para alineamiento de secuencias de ADN y de proteínas.
El inicio del proyecto del genoma humano a ?nales de los ańos 1980 propició un rápido desarrollo de la bioinformática.

En junio del ańo 2000, se logró el primer ensamblaje de la secuencia completa del genoma humano. Aunque este logro pudo parecer el final de un largo camino, en realidad fue solamente el principio.
Por su parte el uso masivo de Internet en los ańos 1990 hicieron posible el acceso inmediato, intercambio y diseminación de datos biológicos; En términos generales la bioinformática ganó prominencia como una disciplina debido al avance en los estudios sobre el genoma que produjeron grandes cantidades de datos biológicos.